library(readxl)
dados <- read_excel("dados_pinus.xlsx")5 Regressão LASSO
A regressçao ridge mantém todas as variáveis no modelo final, memso quando \(k\) é grande. Isso pode ser um problema na interpretação do modelo, por conta da quantidade de variáveis e pelos baixos coeficientes. O lasso pe uma alternativa à regressão ridge que permite obter um modelo final com um subconjunto de variáveis.
Para rodar a regressão Lasso na linguagem R, usaremos o pacote glmnet.
5.0.1 Variáveis
Para ilustrar a regressão ridge, vamos começar com um exemplo em que queremos estudar a relação entre DAP (variável preditora \(X_{1}\)) e Volume (variável dependente Y) com uma amostra de 250 arvores.
- Local: Empresa Duratex Florestal SP
- Amostra: 20 arvores
- IAF : Indice Aerea Foliar
- DAF : Distribuição Angular da Folha
- GAP :
- IDADE : Idade em Meses da arvore
- DAP : Diâmetro a Altura do Peito (1.30 metros do solo)
- ALTURA : Altura da arvore
- ÁEREA BASAL : Area Basal da arvore
5.1 Modelo Regressão LASSO Geral
## Modelo Regressão LASSO Geral
library(caret)
library(glmnet)
set.seed(123)
train_index_lasso <- createDataPartition(dados$VOLUME, p = 0.9, list = FALSE)
dados_treino_lasso <- dados[train_index_lasso, ]
dados_teste_lasso <- dados[-train_index_lasso, ]
x_train_lasso <- model.matrix(VOLUME ~ ., dados_treino_lasso)[, -1]
y_train_lasso <- dados_treino_lasso$VOLUME
x_test_lasso <- model.matrix(VOLUME ~ ., dados_teste_lasso)[, -1]
y_test_lasso <- dados_teste_lasso$VOLUME
# Validação cruzada LASSO
cv_lasso <- cv.glmnet(
x_train_lasso,
y_train_lasso,
alpha = 1,
standardize = TRUE
)
best_lambda_lasso <- cv_lasso$lambda.min
modelo_lasso <- glmnet(
x_train_lasso,
y_train_lasso,
alpha = 1,
lambda = best_lambda_lasso,
standardize = TRUE
)
# Predição
y_pred_lasso <- predict(modelo_lasso, newx = x_test_lasso)
# Métricas
R2_lasso <- cor(y_test_lasso, y_pred_lasso)^2
rmse_lasso <- sqrt(mean((y_test_lasso - y_pred_lasso)^2))
mae_lasso <- mean(abs(y_test_lasso - y_pred_lasso))
mape_lasso <- mean(abs((y_test_lasso - y_pred_lasso) / y_test_lasso)) * 100
# Variáveis selecionadas
coef_lasso <- coef(modelo_lasso)
variaveis_lasso <- rownames(coef_lasso)[
coef_lasso[, 1] != 0 & rownames(coef_lasso) != "(Intercept)"
]
# ---------------- AIC e BIC ---------------- #
y_fitted_lasso <- predict(modelo_lasso, newx = x_train_lasso)
RSS_lasso <- sum((y_train_lasso - y_fitted_lasso)^2)
df_lasso <- modelo_lasso$df[modelo_lasso$lambda == best_lambda_lasso]
n <- length(y_train_lasso)
AIC_lasso <- n * log(RSS_lasso / n) + 2 * (df_lasso + 1)
BIC_lasso <- n * log(RSS_lasso / n) + log(n) * (df_lasso + 1)
# Resultados
cat("\n--- Modelo LASSO ---\n")
--- Modelo LASSO ---cat(
"R² =", R2_lasso,
"\nRMSE =", rmse_lasso,
"\nMAE =", mae_lasso,
"\nMAPE =", mape_lasso,
"\nAIC =", AIC_lasso,
"\nBIC =", BIC_lasso
)R² = 0.9199676
RMSE = 12.2659
MAE = 10.5483
MAPE = 23.57098
AIC = 1055.38
BIC = 1075.903cat(
"\nVariáveis selecionadas:",
paste(variaveis_lasso, collapse = ", "),
"\n"
)
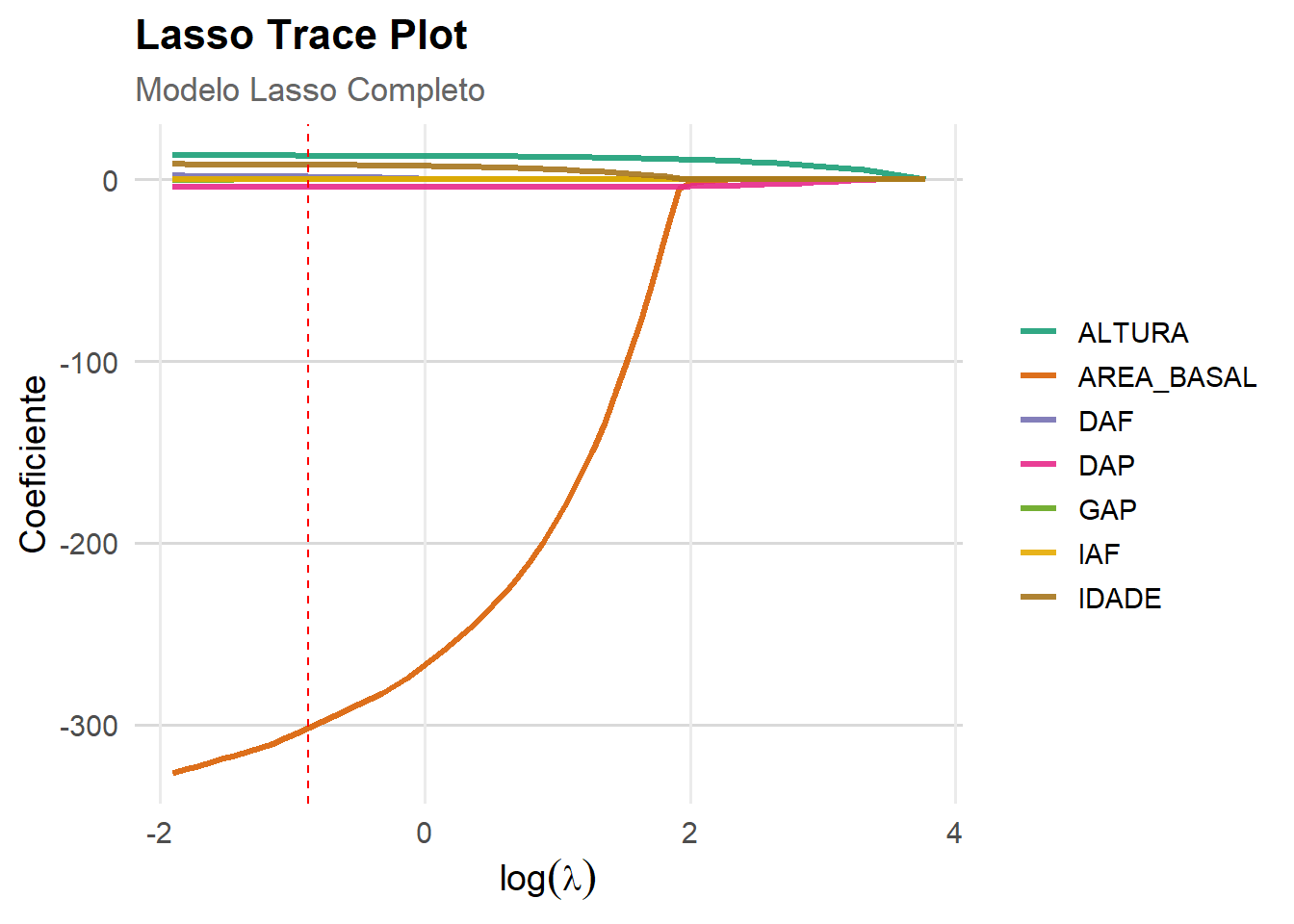
Variáveis selecionadas: IDADE, DAP, ALTURA, DAF, AREA_BASAL 5.2 Lasso Trace Plot
library(dplyr)
library(tidyr)
library(ggplot2)
library(glmnet)
lasso_seq <- glmnet(x_train_lasso,
y_train_lasso,
alpha = 1,
standardize = TRUE)
# Índice do lambda ótimo
id_best <- which.min(abs(lasso_seq$lambda - best_lambda_lasso))
# Coeficientes no lambda ótimo
coef_best <- as.matrix(lasso_seq$beta)[, id_best]
# Variáveis selecionadas (≠ 0)
vars_selected <- names(coef_best[coef_best != 0])
# Construir data frame dos coeficientes ao longo do caminho
df_lasso_path <- as.data.frame(t(as.matrix(lasso_seq$beta)))
df_lasso_path$log_lambda <- log(lasso_seq$lambda)
# Manter apenas variáveis selecionadas no modelo final
df_lasso_path <- df_lasso_path %>%
select(log_lambda, all_of(vars_selected)) %>%
pivot_longer(
cols = -log_lambda,
names_to = "Variavel",
values_to = "Coeficiente"
)
# Gráfico LASSO TRACE – MODELO ESCOLHIDO
ggplot(
df_lasso_path,
aes(x = log_lambda, y = Coeficiente, color = Variavel)
) +
geom_line(size = 1.3) +
geom_vline(
xintercept = log(best_lambda_lasso),
linetype = "dashed",
linewidth = 1,
color = "black"
) +
labs(
title = "LASSO Trace Plot",
subtitle = expression(paste(
""
)),
x = expression(log(lambda)),
y = "Coeficiente"
) +
scale_color_brewer(palette = "Dark2") +
theme_minimal(base_size = 14) +
theme(
plot.title = element_text(face = "bold", size = 16),
plot.subtitle = element_text(size = 13, color = "gray40"),
legend.title = element_blank(),
panel.grid.minor = element_blank()
)
5.3 MODELO MLP (REDE NEURAL)
library(caret)
library(nnet)
library(dplyr)
set.seed(123)
train_index_nn <- createDataPartition(dados$VOLUME, p = 0.9, list = FALSE)
dados_treino_nn <- dados[train_index_nn, ]
dados_teste_nn <- dados[-train_index_nn, ]
preproc <- preProcess(dados_treino_nn[, -which(names(dados) == "VOLUME")],
method = c("center", "scale"))
x_train_nn <- predict(preproc, dados_treino_nn)
x_test_nn <- predict(preproc, dados_teste_nn)
set.seed(123)
ctrl <- trainControl(method = "cv", number = 10)
grid_mlp <- expand.grid(
size = c(3, 5, 7),
decay = c(0.001, 0.01, 0.1)
)
modelo_mlp <- train(
VOLUME ~ .,
data = x_train_nn,
method = "nnet",
tuneGrid = grid_mlp,
trControl = ctrl,
linout = TRUE,
trace = FALSE,
maxit = 500
)
y_pred_mlp <- predict(modelo_mlp, newdata = x_test_nn)
R2_mlp <- cor(dados_teste_nn$VOLUME, y_pred_mlp)^2
rmse_mlp <- RMSE(y_pred_mlp, dados_teste_nn$VOLUME)
mae_mlp <- MAE(y_pred_mlp, dados_teste_nn$VOLUME)
cat("\n--- REDE NEURAL (MLP) ---\n")
--- REDE NEURAL (MLP) ---cat("R²:", R2_mlp,
"\nRMSE:", rmse_mlp,
"\nMAE:", mae_mlp,
"\nMelhores parâmetros:",
"\nNeurônios ocultos:", modelo_mlp$bestTune$size,
"\nDecay:", modelo_mlp$bestTune$decay,
"\n")R²: 0.9180618
RMSE: 12.37432
MAE: 10.42029
Melhores parâmetros:
Neurônios ocultos: 3
Decay: 0.1